Сегодня я хочу рассказать о том, как я писал отчеты на R, с чем сталкивался и как решал проблемы, которые возникали по ходу разработки. Отчеты были в формате PDF и запускались из Python в Camunda.
1. Запуск отчетов на R
Первое, с чем пришлось столкнуться — это желание заказчика запускать генерацию отчетов на R из Python. Точнее из Python запускали subprocess.Popen, который запускал R script. R script, в свою очередь, запускал одну из функций генерации того или иного отчета, которая была частью нашего проекта, написанного как пакет на R. Разницу между пакетом и обычными скриптами на R я описал тут — ссылка. Можно сразу дергать функции R и мой коллега пытался переписать вызов отчетов из Python, но то ли из-за проблем с окружением на сервере, то ли из-за Camunda, в которой это все запускалось, такой способ отлично работал локально, но не работал на нашем боевом окружении. Минусом же вызова R через subprocess.Popen является то, что Python вызывает R скрипт через shell, а уже внутри этого скрипта дергается функция пакета R.

Параметры для отчета тоже приходится передавать через shell и уже в R script файле так же их читать как будь то их передают через командную строку.
Часть кода на Python:
parameters = { "param1": param1, "param2": param2, "param3": param3 } ... command_list = ["Rscript", path_to_r_script] + [f"--{key}={value}" for key, value in parameters.items()] with subprocess.Popen( command_list, stdout=subprocess.PIPE, stderr=subprocess.PIPE, cwd=work_dir ) as sub_prc_response: stdout, stderr = sub_prc_response.communicate() return_code = sub_prc_response.returncode Script на R, где ourpackage название нашего пакета:
options(warn=-1) library(ourpackage) library(optparse) options = list( make_option("--param1", help = "first parameter"), make_option("--param2", help = "second parameter"), make_option("--param3", help = "third parameter"), ) cli_arguments = parse_args(OptionParser(option_list = options)) generate_report(param1 = cli_arguments$param1, param2 = cli_arguments$param2, param3 = cli_arguments$param3) Возникает вопрос как это все тестировать и отлаживать. У нас часть кода на Python, а часть на R. Можно использовать JupiterHub, но наши администраторы настроили его так, что код на Python мы могли вызвать, а вот код на R нет. Мотив был — экономия памяти и ресурсов. В итоге тестировали через RStudio. В ней можно создать файл типа Python:
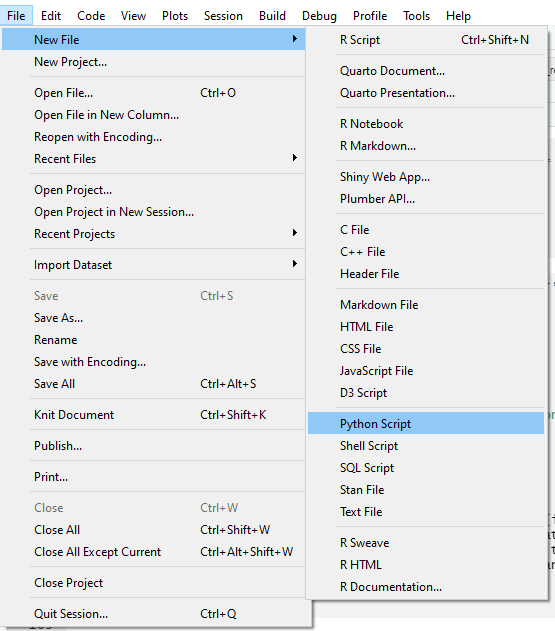
И уже внутри этого файла вызвать функцию python, которая, в свою очередь, вызовет генерацию отчета на R.
Пример вызова:
from our_project.workflow.generate_report_one import report_one_executor task = { "variables": { "param1": {"value": "value1"}, "param2": {"value":"value2"}, "param3": {"value":"value3"} } } report_one_executor(task)Чтобы проверить и отладить сам R script файл, его можно запустить из Terminal в RStudio. Для этого его вам придется положить внутрь вашего проекта, хотя бы на время теста и отладки. Можно держать его и вне проекта, если вам это позволяют настройки окружения, в котором вы работаете. У меня не было такой возможности, поэтому я размещал script файл в подпапке внутри R папки проекта, так как в пакет содержимое подпапок не попадает и, конечно же, не коммитил эту попдпапку в репозиторий. Команду запуска отчета через script надо писать в Terminal. Это вкладка на нижней панели в RStudio.
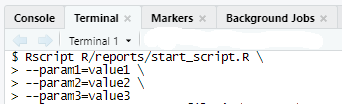
Пример запуска из shell:
Rscript R/reports/start_script.R \ --param1=value1 \ --param2=value2 \ --param3=value3В коде, для генерации отчетов, надо указать путь к RMD файлу, на основе которого будет строиться отчет. Пример функции, которая строит отчет ниже, при условии что RMD файл лежит в inst/reports:
output_rmd <- function(output_report_file = "test", output_report_dir = NULL, output_type = "DOCX", params_list = NULL) { rmd_file = "test-report.Rmd" report_rmd_folder <- system.file("reports", package = "myRTestPrj") rmd_input <- paste(report_rmd_folder, rmd_file, sep = "/") rmarkdown::render( rmd_input, output_file = output_report_file, output_dir = output_report_dir, params = params_list ) }2. Конфликт библиотек
При сборке пакета часто можно увидеть сообщения типа:
replacing previous import ‘flextable::rotate’ by ‘ggpubr::rotate’ when loading ‘our_project’В этом сообщении говорится, что если явно для функции rotate не указать название библиотеки, то будет вызываться ggpubr::rotate. Это происходит из-за того, что в разных пакетах есть функции с одинаковыми именами. Чтобы эти сообщения не выводились можно указать какие функции из каких библиотек должны грузиться, а какие нет. У нас в проекте для этого в папке R был создан файл global_imports_pkg.R в котором прописывались именно те функции, которые нам нужны.
# Global libraries #' @importFrom data.table dcast melt rbindlist #' @import ggplot2 #' @rawNamespace import(ggpubr, except=c(font)) #' @importFrom grDevices rgb colorRampPalette #' @rawNamespace import(huxtable, except=c(add_rownames,theme_grey)) NULLНо это потенциально может привести к другой, более коварной ошибке. Пусть у вас в global_imports_pkg.R написанно так:
#' @importFrom data.table melt rbindlistА в коде вы вызываете функцию dcast, которой нет в строчке выше. Есл вы запустете функцию из под RStudio, просто написав в консоли:
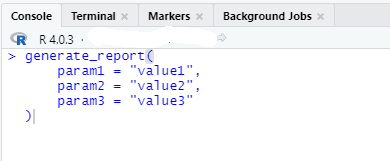
У вас все будет работать, так как локально вы себе инсталлировали весь пакет data.table, а вот при попытке вызвать эту же функцию из Python, у вас будет ошибка, так как в проекте у вас написанно, что в наш пакет нужно подгрузить только 2 функции из data.table — это melt и rbindlist. Ту же ошибку вы можете получить на сервере, хотя локально все будет работать.
Похожее поведение можно так же получить, если забыть добавить используемый вами сторонний пакет в файл DESCRIPTION:
... Imports: highcharter, statnet.common, hablar Suggests: devtools, ...При запкуске локально в RStudio все будет работать, так как вы явно установили этот пакет локально, но вот при вызове вашего пакета сторонним кодом или средой вы получите ошибку.
3. Утечка памяти в Rmarkdown::render
При генерации больших отчеов в PDF формате возникает ошибка, если посмотреть в терминале на процесс генерации шаблона, то видно как он отъедает всю доступную память и падает. Для решения этой проблемы мы резали отчет на части и потом их склеивали. Для этого использовали qpdf::pdf_combine. Проблема с утечкой памяти обсуждается как минимум тут. Какого-то более простого решения найти не получилось, хотя сил и времени было потраченно немало.
4. Latex
Для форматирования pdf отчетов использовали Latex. Начальный шаблон для отчета был взят тут.
Код на R для генерации отчета с шаблоном Latex:
rmarkdown::render( rmd_input, output_format = "pdf_document", output_file = output_file, output_dir = output_report_dir, params = params, output_options = list( template = paste0(report_rmd_folder, "/assets/custom.latex"), clean = TRUE ) )Так же непосредственно в шапку RMD файла можно добавить команды для форматирования документа:
--- title: header-includes: \usepackage{graphicx} \usepackage{fancyhdr} \pagestyle{fancy} \color{ecbdarkblue} \color{ecbbgr} % Head \fancyhead[C]{} \fancyhead[L]{} \fancyhead[R]{} % Remove header line \renewcommand{\headrulewidth}{0pt} % Page margins \usepackage{geometry} \geometry{ a4paper, left=30px, top=10mm, headsep=5mm, right=50px } % Titles \usepackage{titlesec} \titlespacing\section{0mm}{7pt plus 4pt minus 2pt}{28pt plus 2pt minus 2pt} \titlespacing\subsection{6mm}{-7pt plus 4pt minus 2pt}{0pt plus 2pt minus 2pt} \titlespacing\subsubsection{6mm}{12pt plus 4pt minus 2pt}{0pt plus 2pt minus 2pt} % Section and subsection titles \sectionfont{\fontfamily{phv}\selectfont\LARGE\bfseries\color{ecbdarkblue}} \subsectionfont{\fontfamily{phv}\selectfont\normalsize\mdseries\color{white}} \subsubsectionfont{\fontfamily{phv}\selectfont\scriptsize\mdseries\color{white}} \color{black} % Line spacing \usepackage{setspace} \setstretch{0.6} % Section color \usepackage{xcolor} \usepackage{framed} \colorlet{shadecolor}{ecbbgr} % Footer \fancyfootoffset[R]{-2mm} \renewcommand{\footrulewidth}{0.4pt}\color{ecbdarkblue} \rfoot{\vspace{0.5mm}\Large\color{ecbdarkblue}\colorbox{ecbbgr}{ S \color{white}\thepage}} \cfoot{\vspace{0.01mm}\scriptsize\bfseries\hspace{420px} ECB \\ \scriptsize\bfseries\color{black}\hspace{390px} DG-S/EA/GBS\\ \scriptsize\bfseries\color{ecbdarkblue}\hspace{395px} `r format(Sys.Date(), format="%d %b %Y")`} \lfoot{} output: pdf_document: keep_md: no keep_tex: no latex_engine: pdflatex number_sections: false --- ```{r setup, include=FALSE} # some code here... ```Подробно команды Latex я не буду разбирать, так как достаточно посмотреть на код в тех или иных блоках и понять, как надо его поправить, чтобы изменить форматирование. Во многом я опирался на этот сайт когда форматировал документ.
Можно так же гибко настроить какие ошибки и сообщения будут писаться в отчет. Это делается командой:
knitr::opts_chunk$set(echo = FALSE, warning = FALSE, message = FALSE, error = TRUE)Можно эти настройки так же включать и отключать в шапке chunk:
```{r our_chunk, eval = TRUE, results='asis', echo=FALSE, warning=FALSE, message=FALSE, error=TRUE}5. Заглушки для внешних библиотек при написании Unit тестов
Для вызова вункций из внешних библиотек, написанных на Python мы использовали reticulate.
Пример вызова внешней функции:
get_python_func <- function(param1) { pm <- reticulate::import("our_project.core.python_functions") return(pm$get_python_func(param1)) }Тест — заглушка для такой функции:
test_that("get_python_func", { stub(get_python_func, "reticulate::import", list(get_python_func = function(...) TRUE)) res <- get_python_func(param1 = "value1") expect_equal(res, TRUE) })6. Отладка кода
При отладке кода есть возможность скопировать значения внутренних переменных в глобальную область памяти и напрямую вызвать нужную нам часть кода с определенными значениями переменных для этого кода.

На картинке выше в верхнем правом углу в поле Data есть переменная df. Чтобы скопировать её в глобальную область надо написать в Console:
assign("df", value = df, envir = .GlobalEnv)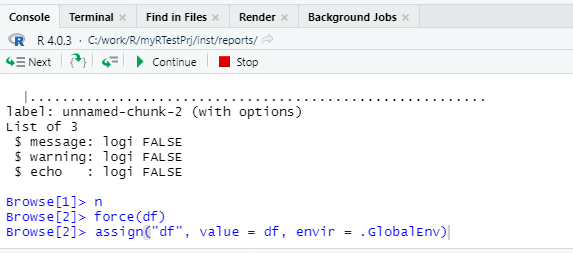
И выполнить эту команду — нажать ENTER.
После этого можно выделить тот код который мы хотим протестировать с этой локальной переменной и запустить его — CTRL+ENTER.
Дело в том, что отладка в RMD файле не работает и вся логика по возможности выносится в функции, которые находятся в файлах *.R. К этому ещё добавляется не высокая скорость генерации отчетов из RMD файла. В таких условиях каждый раз делать DEBUG не удобно. Работает все медленно и участки кода в RMD не отладить. А с установкой значений переменных в глобально области можно проверить любой участок кода, даже если он находится непосредственно в RMD файле.
7. Использование классов в проекте
Мы использовали ReferenceClasses, решив, что они больше всего нам подходят. Правда, их невозможно отладить инструментами RStudio. Но есть стандартные функции отладки, с помощью которых сама отладка возможна:
s$trace(class_method, browser) s$untrace(class_method, browser) debug(s$class_method)Где s — это экземпляр класса, а class_method — это метод класса. Но он оказался не очень удобным и мы отлаживали с помощью переменных в глобальной области видимости.
8. Прочие нюансы проекта
-
Библиотека для работы с данными для отчетов — dplyr
-
Чтобы создать список из входящих параметров функции использовали следующий код:
# create list with input parameters params <- c(as.list(environment()))-
Удалить параметры или параметр из глобального окружения можно с помощью команды rm
-
Статический анализатор кода — lintr
-
Для автоматической записи документации в Confluence использовали библиотеку conflr
-
Таблицы в отчетах делали с помощью felxtable
Заключение
Это статья — памятка, в которой я описал ключевые вещи проекта, которые я не хотел бы забыть и которые, на мой взгляд, были бы полезны тем, кто работает с аналогичными проектами на языке R. Возможно что-то можно улучшить, а чего-то избежать, но не хотелось бы «Изобретать велосипед заново», начиная новый проект на R. В заключении хотел бы пожелать всем успехов, а также хороших и интересных проектов.
ссылка на оригинал статьи https://habr.com/ru/post/691938/
Добавить комментарий